武汉金开瑞生物工程有限公司品牌商
12 年
手机商铺
- NaN
- 0.5
- 0.5
- 1.5
- 0.5
公司新闻/正文
【详解】如何使用Skyline从DDA数据中的MS1扫描提取定量信息
2939 人阅读发布时间:2021-08-02 14:52
Skyline是一个免费的开源Windows客户端应用程序,支持构建选择性反应监测(SRM)/多反应监测(MRM)、平行反应监测(PRM-目标MS/MS),数据非依赖型采集(DIA/SWATH)和MS1定量(如label-free定量)的DDA,并对所得的质谱数据进行分析。
本文将详细阐述:如何从数据依赖型串联质谱获得的DDA数据的MS1 谱图中提取时间-强度色谱峰来进行肽段定量。这里先从Skyline软件的下载安装开始,帮助您快速入门,迅速了解该软件一些功能,为以后的深度学习打下一个基础。
下载网址:
https://skyline.gs.washington.edu/labkey/project/home/software/Skyline/begin.view
网站界面如下图,点击红色箭头指示的链接下载即可。

下载后双击setup.exe可执行文件,根据提示逐步完成安装。
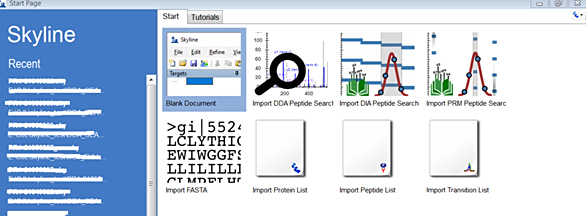
双击安装好的Skyline桌面图标,运行后的界面如下。点击“blank document”就可以开始Skyline参数配置及定量分析。
4.1 肽段设置(Peptides Settings)
4.1.1 创建背景蛋白库(Background proteome)
点击“Settings→Peptide Settings”进入“Digestion”选项卡。蛋白水解酶<Enzyme>为胰蛋白酶,最大漏切数目<Max missed cleavage>一般为2。

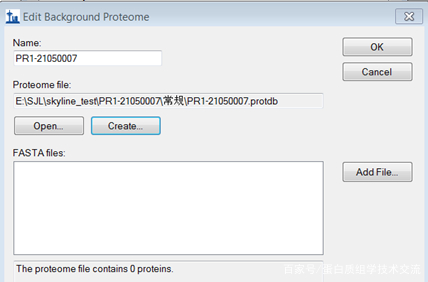
在<Background proteome>中构建背景蛋白库,单击下拉框选择<Add>,进入编辑界面。在<Name>中为蛋白库命名,如果是第一次创建背景蛋白库,单击<Create>设置背景蛋白库的存储路径,如果已有现成的背景库,点击<Open>打开。此时<Add File>按钮由灰色转变为激活状态,单击添加Fasta文件。最后单击<OK>完成背景蛋白库设置。
4.1.2 构建谱图库(Spectral Library)
蛋白库生成主要用到*.group文件。单击“Library”选项卡,如果已经有现存的谱图库,直接勾选即可,否则单击<Build>进入谱图库构建界面。
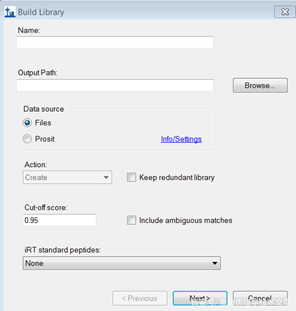
在<Name>中为谱图库命名,在<Output Path>中选择谱图库的保存路径。勾选“Keep redundant library”可选框,保留冗余库,目的是让库中保留尽可能多的谱图信息。填写<Cut-off score>为0.95,即设定FDR为0.05。
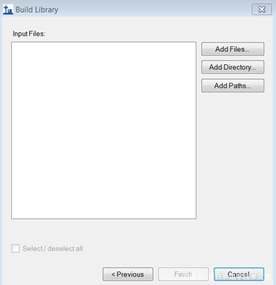
单击<Next>进入数据导入界面。单击<Add Files>添加构建谱图库的文件(一般为某种搜索软件搜索完DDA数据后的结果,这里使用的是Proteinpilot软件搜索,所以建库文件是.group),单击”Finish”完成谱图库构建。此步骤一般需要几分钟,先生成与每个*.group对应的*.xml文件,再执行导入,由*xml文件构建谱图库。在<Libraries>中确保本次构建的谱图库被选中,且无其他不必要的库。
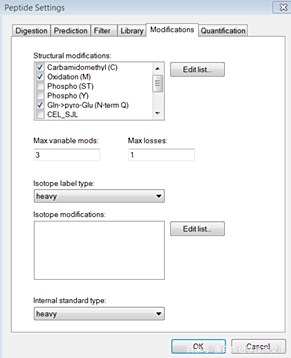
4.1.3 修饰设置(Modifications)
点击“Modifications”选项卡,在<Structureal modifications>中选择修饰类型,在没有特殊要求的情况下仅勾选以下4种修饰:
Carbamidomethyl (C)
Oxidation (M)
Gln→pyro-Glu (N-term Q)
Acetyl (N-term)
其他设置保持默认。
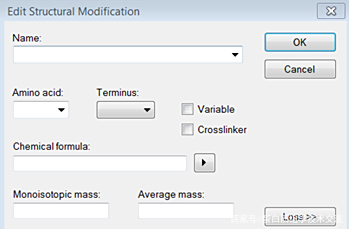
若<Structureal modifications>中没有想要的修饰,点击“Edit list->Add”构建修饰。<Name>填写修饰名,<Amino acid>指发生修饰的氨基酸,<Terminus>在氨基酸的C端 or N端发生修饰,<Variable>是否是可变修饰,<Chemical formula>填写修饰的化学式,可点击旁边小三角进行选择。完成后点击<Ok>即可。
4.2 离子设置
点击“Settings→Transition Settings”,进入“Prediction”选项卡。

前体离子质量下拉框<Precursor mass>选择单一分子量“Monoisotopic”
子离子质量下拉框<Product mass>选择单一分子量“Monoisotopic”
碰撞能量<Collision energy>选择“ABI TOF 5600”(根据所使用的质谱填写)
去族电压<Declustering potential>择“None”
优化库<Optimization library>选择“None”
补偿电压<Compensation Voltage>选择“None”
点击<Filter>按照下图设置:

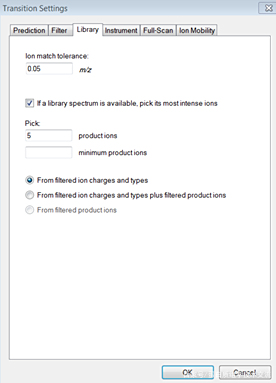
点击<Library>按照下图设置:
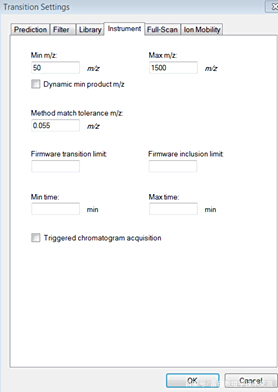
点击<Instrument>按照下图设置:
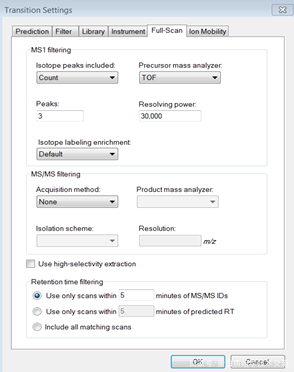
点击<Full-Scan>按照下图设置:
4.3 定量分析
4.3.1 载入谱图库
点击“View→Spectral Libraries”,进入谱图浏览界面。
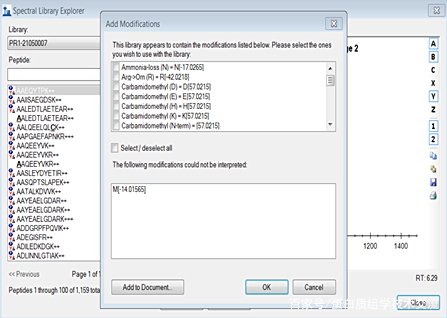
较之前的设置而言(4种),谱图库中一般会含有更丰富的修饰类型,所以会提示是否考虑这些修饰,无特殊需求不考虑。
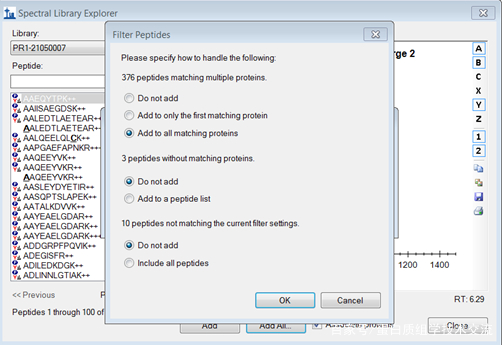
这里展示的是谱图库中所有肽段的信息,勾选<Associate proteins>,关联每一肽段属于哪一个蛋白质,点击<Add All>,即可将谱图库中的肽段导入“Targets”一栏中。
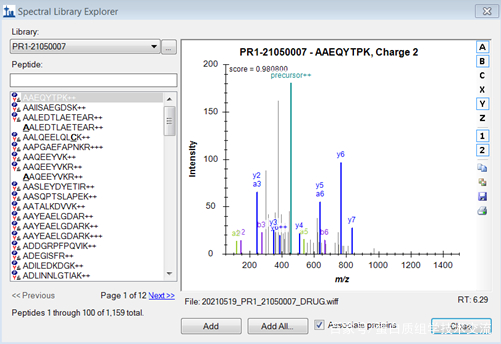
完成后会提示与蛋白质匹配上的肽段数,未匹配上的肽段数以及被过滤掉的肽段数。
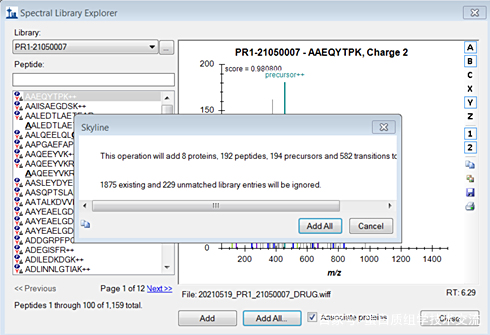
单击“OK”跳出对话框如下,会提示总体的蛋白,肽段及离子数目。
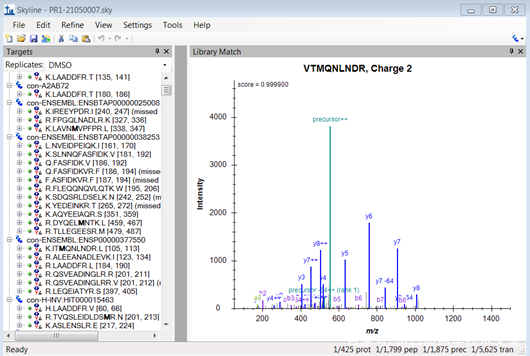
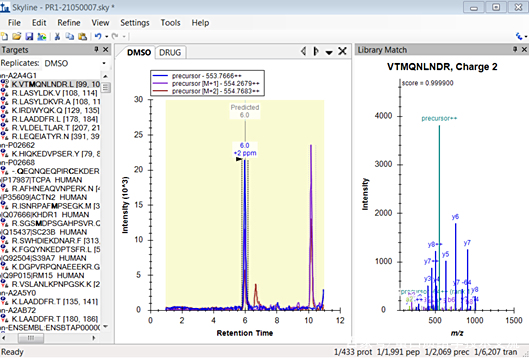
在主界面中,左侧<Targets>显示所要研究的目标肽段,右侧显示谱图库信息,若是空白则可点击“View->Library Match”查看。
4.3.2载入DDA数据
点击“File→Import→Result”,进入结果载入界面,选择”Add single-injection replicates in files”,单击“OK”,载入DDA模式下生成的.wiff文件。
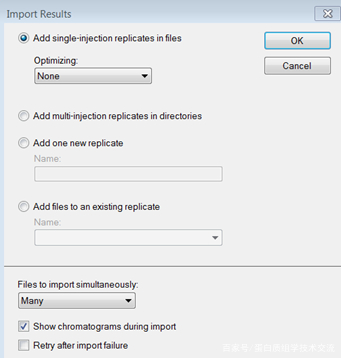
完毕,会提示是否去除所有wiff文件名称中开头重复的部分。完成后主界面展示了Targets、各样本DDA模式下母离子的XIC和Labrary Macth。
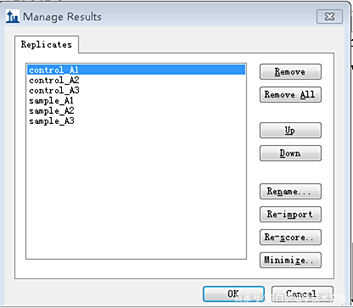
4.3.3 样本名称更改
点击“Edit→Manage Result”,可用于样品名称更改,以便后期分析。
至此,DDA数据的输入与分析暂时结束,记得点击“File->Save”保存到.sky哦。
4.4 输出定量结果
点击“File→Export →Report”输出定量结果。
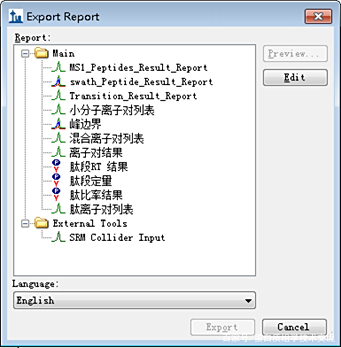
可点击“Edit-->Add”,新增一个结果输出的样式,添加想要输出的对象。最后输出肽段定量表(*.csv格式),作为后续分析的主要数据来源。
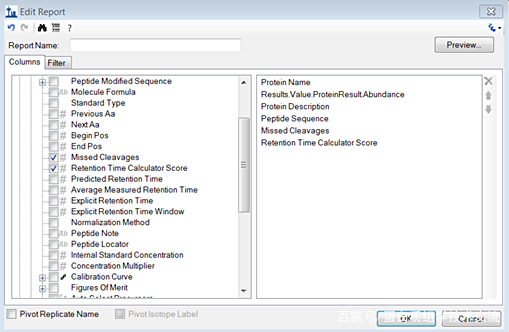
至此,使用Skyline处理DDA数据的流程就暂时告一段落,现在可以尝试着去构建一个属于自己的Skyline文档了。
武汉金开瑞生物相关技术服务推荐
► 服务内容:
| 服务项目 | 细分 | 适用范围 |
|---|---|---|
| 发现蛋白质组学 | 单一蛋白鉴定 | 目标蛋白鉴定、蛋白混合物鉴定 |
| 蛋白全谱鉴定 | 某一生理状态下组织、细胞或者细胞器中所有表达蛋白质的鉴定 | |
| 比较蛋白质组学 | Label-free定量 | 适合大样本量的定量比较,对无法用标记定量实现的实验设计,用Label-free技术。可应用于药物作用靶点研究、疾病标志物筛选、植物胁迫/抗逆研究、作用机制研究、物种蛋白质草图构建等 |
| iTRAQ/TMT定量 | 一次能标记8样本(iTRAQ)或10样本(TMT),可应用于药物作用靶点研究、疾病标志物筛选、植物胁迫/抗逆研究、作用机制研究、物种蛋白质草图构建等 | |
| SWATH/DIA定量 | 适合检测细菌等复杂度较低的样品,可以和MRM HR 技术联合使用发现生物标志物,可以和TAP技术联合使用鉴定相互作用蛋白 | |
| 修饰蛋白质组学 | 磷酸化修饰 | 鉴定样品中发生磷酸化/琥珀酰化/糖基化/乙酰化/巴豆酰化修饰的蛋白质以及相应的磷酸化/琥珀酰化/糖基化/乙酰化/巴豆酰化修饰位点 |
| 琥珀酰化修饰 | ||
| 糖基化修饰 | ||
| 乙酰化修饰 | ||
| 巴豆酰化修饰 | ||
| 靶向蛋白质组学 | MRMHR /PRM | 适用于高通量定量蛋白组学后,进行目标蛋白验证;目标蛋白质/肽段相对或绝对定量,蛋白质翻译后修饰的定性定量研究 |
| 多肽组学 | 多肽组学鉴定 | 适合研究毒液、尿液、血液以及其他分泌液样本 |
| 多肽组学Label-free定量 |
注:金开瑞可提供线粒体蛋白质组学、叶绿体蛋白质组学、膜蛋白质组学、石蜡包埋蛋白质组学、4D蛋白质组学、临床大队列蛋白质组学整体解决方案等技术服务
► 部分客户已发表文献:
- Photo-Powered Artificial Organelles for ATP Generation and Life-Sustainment. Advanced Materials(IF=21.95), 2018.(合作技术:Label-free)
- Photocatalyzing CO2 to CO for Enhanced Cancer Therapy. Advanced Materials(IF=21.95), 2017.(合作技术:iTRAQ)
- Exome-wide analysis identifies three low-frequency missense variants associated with pancreatic cancer risk in Chinese populations. Nature Communications(IF=12.353), 2018.(合作技术:磷酸化iTRAQ)
- Optically-controlled bacterial metabolite for cancer therapy. Nature Communications(IF=12.353), 2018.(合作技术:iTRAQ)
- Combined spectroelectrochemical and proteomic characterizations of bidirectional Alcaligenes faecalis-electrode electron transfer. Biosensors & Bioelectronics(IF=8.173), 2018.(合作技术:SWATH)
- Chemical Signals Stimulate Geobacter soli Biofilm Formation and Electroactivity. Biosensors & Bioelectronics(IF=8.173), 2019. (合作技术:SWATH)
► 联系方式:
电话: 027-62431110
Q Q: 3013422302
微信: 15327327477
邮箱:marketing@genecreate.com
网址: http://www.genecreate.cn
地址: 武汉市东湖高新区高新大道666号生物创新园B4栋2楼